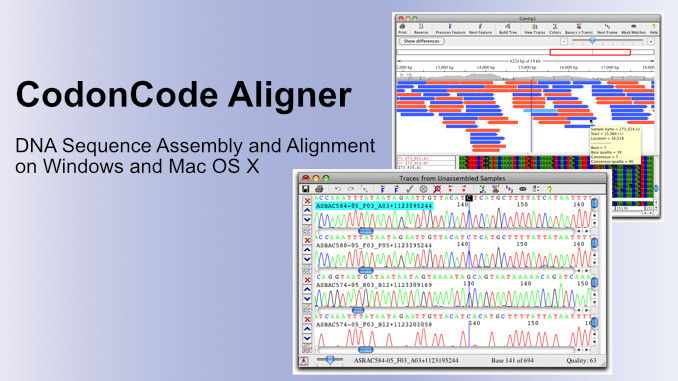
ユニポスWEBサイトに、DNAの配列アセンブリングと配列アラインメントのためのプログラム CodonCode Aligner のページを追加しました。
CodonCode Aligner は、シーケンスアセンブリ、コンティグの編集、変異検出などを実施するためのプログラムです。Phred-Phrapとの互換性があり、シーケンスクオリティスコアに完全に対応しています。
複雑なコマンドラインオプションや Perlプログラミング習得の必要なく、ベースコーリングや配列アセンブリのための最新のアルゴリズムを活用することができます。また学習が容易なユーザーインターフェースも特徴です。
CodonCode Aligner 機能について
・Import sequences from text files
・Import sequences from ABI, SCF, and FASTQ files
・End clip
・Vector trim
・Assemble contigs
・Align to a reference sequence
・Align contigs to each other while keeping the links to the traces
・Assemble or align in groups, based on sample names
・Find heterozygous mutations
・Analyze heterozygous insertions and deletions
・Define regions of interest (“features”), for example low quality consensus regions
・Quickly navigate between user-defined features
・Generate phylogenetic trees and restriction maps
・Run Phred and Phrap directly from Aligner projects
・Export sequences and features
・See difference tables and protein translations
・Design primers
・Assemble bacterial genomes and small NGS sequencing projects
・Find enzymes for RFLP analysis & create virtual gel
・Analyze methylated sequences & view raw trace data
※CodonCode Alignerは、Windows と Mac OS X に対応しています
| ■商品の詳細、お問い合わせはこちら CodonCode Aligner / DNAの配列アセンブリングと配列アラインメントのためのプログラム メーカー (CodonCode Corporation) WEBサイト |